Quizá este sea uno de los descubrimientos más emocionantes de la biología. Algunos virus han cambiado la codificación de su ADN y poseen un genoma no visto en todos los dominios de la vida. Los científicos lo llaman el genoma Z.
La dinámica de la vida
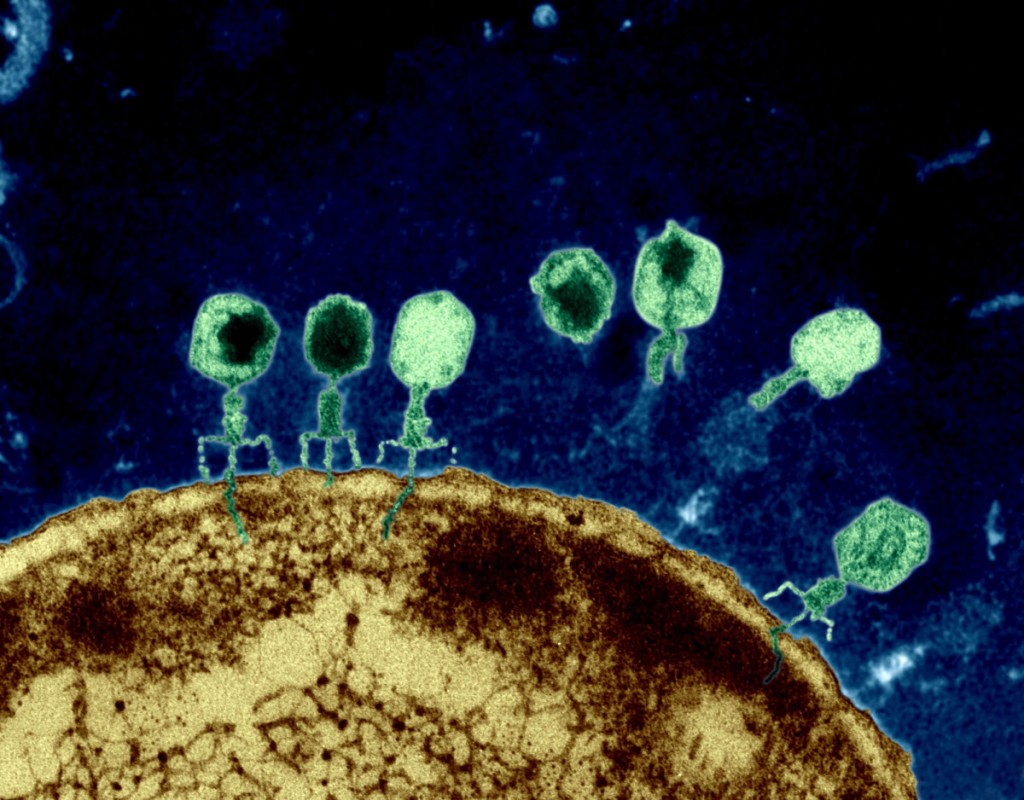
Desde que las bacterias colonizaron la Tierra, han librado una guerra permanente con un mortal enemigo, los bacteriófagos. No conocemos con exactitud su origen pero sabemos cuál es su misión. En 1915, el bacteriólogo Frederick Twort sentenció: “hay virus que infectan bacterias y las matan”. Como los otros virus, los bacteriófagos tienen vida intracelular obligada, por ello necesitan infectar a bacterias y arqueas.
La vida en la Tierra depende de un código de cuatro letras, ATCG, cada una de las cuales representan los nucleótidos del ADN. A, para adenina; T, para timina; C, para citosina y; G, para guanina. Para formar la doble hélice del ADN, estas bases nitrogenadas se disponen en pares; así, unidas por puentes de hidrógeno, A va con T y, C con G. Dicha dinámica se repite en cada ser que habita la Tierra, incluidos los virus… ¿o no?
Análogos de ácidos nucleicos
En 1977, se descubrió el cianófago S-2L, un virus especializado en la infección de cianobacterias que, increíblemente tenía todas las moléculas de adenina (A) sustituidas por un molécula híbrida entre adenina y guanina, llamada 2-aminoadenina y representada por la letra Z. En efecto, su genoma posee el alfabeto ZTCG.
Esto fue increíblemente sorprendente porque no se conocía la existencia de análogos de los ácidos nucleicos. Los científicos explicaron que en la guerra entre fagos y bacterias, los virus necesitan resistir las defensas de las células bacterianas. Usualmente, A y T se encuentran enlazadas por dos puentes de hidrógeno; pero, el enlace Z y T posee tres, haciéndolo más resistente a la degradación por las nucleasas de las bacterias.
La emoción de aquella época se vio frustrada por la ausencia de más bacteriófagos con genoma Z y por la dificultad de cultivar el 2S-L en laboratorio. Sin embargo, las esperanzas de detectar más nucleobases permaneció intacta. El pasado 30 de abril en la revista Science se publicaron tres artículos que documentan la amplia investigación realizada por tres grupos de científicos y revelan lo siguiente: que el 2S-L no es el único, cómo funciona el genoma Z y cómo se ensambla.
Investigaciones revolucionarias
El equipo liderado por Yan Zhou, de la Universidad de Tianjin, junto al equipo de Dona Sleiman, del Instituto Pasteur, identificaron primero dos proteínas encargadas de formar la base híbrida Z. Las denominaron PurZ y PurB. Simultáneamente, el equipo liderado por Valerie Pezo de la Universidad Paris-Saclay, analizó la enzima DpoZ, cuya función es ensamblar todo el genoma Z.
Los tres equipos reunidos tuvieron el trabajo de buscar en una amplia base de datos de secuencias genéticas las secuencias relacionadas con la codificación de PurZ, PurB y DpoZ y comprobar así si otros virus las tenían. De acuerdo con sus hallazgos una gran variedad de virus poseen los genes para las tres moléculas.
Es decir, con su trabajo confirmaron la existencia de todo un grupo de bacteriófagos con un genoma análogo. Asimismo, les permite conocer cómo funciona el genoma Z y la vía biosintética de la 2-aminoadenina, Z. Finalmente, nos muestra que cuando se trata de sobrevivir, los virus son capaces hasta de cambiar su genoma.